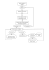fenotipado-selectivo.. - maiz hd
Transcripción
fenotipado-selectivo.. - maiz hd
FENOTIPADO SELECTIVO COMO ESTRATEGIA PARA REDUCIR COSTOS Y TIEMPO OPERATIVO EN LA LOCALIZACION DE QTL´s Giomi G.M., Presello D.A., Rodriguez M.A., Fauguel C., Fernandez M. Estación Experimental INTA Pergamino. CC 31. 2700 – Pergamino. Provincia de Buenos Aires. Argentina. [email protected] Techniques of selective phenotyping allow to choose a reduced subset of progenies in mapping populations, minimizing the loss of information and sensitivity for localization of QTLs. These techniques are used for characters that have high operating costs in labor and supplies. In previous studies were mapped QTLs for resistance to Fusariumverticillioides in a population of 298 lines (F4:F5) derived from L4637 × L4673. These parental lines differ in resistance to Fusarium spp. and at least in two of its components, thickness and content of ferulic acid in the pericarp. This work was carried out with the aim of choosing a subset of lines able to detect the same QTLs for disease resistance minimizing loss of information for mapping both components. We develop a software that provided the matrix analysis of the genetic composition of individuals, following Jannink (2005), method called uniRec, to select a subgroup of 120 lines. For each group of lines, the genetic map was built with the MapDisto program v1.7.5.1, performed statistical analysis with the SAS software v5.1 and carry out an analysis of QTLs with the multi-character mapping by composite interval procedure of winQTLcart v2.5 program. The loss of information in relation to molecular data was relatively low considering that we only use about 2/5 of the initial population. Mapping of the subset of 120 lines identified the same 5 QTLs for resistance to disease, located on chromosomes 1, 2, 3 and 5, that had been identified by using data from the whole population. These results indicate that, while there was a loss in precision, the major QTLs were identified in both populations and therefore this subset of lines is appropriate to map QTLs for both disease resistance components. Key words: ear rot, Fusarium, resistance components, selective phenotyping, quantitative trait loci Palabras clave: podredumbre de espiga, Fusarium, componentes de resistencia, fenotipado selectivo, loci de carácter cuantitavo (QTL) INTRODUCCION Existen varias especies de hongos pertenecientes a los géneros Fusarium, Diplodia, Aspergillus y Penicillium que afectan al maíz (Zea mays L.) produciendo enfermedades conocidas como podredumbres de espiga.Se identificaron fuentes de resistencia a la invasión de F. verticillioides y la subsecuente acumulación de fumonisinas en el germoplasma local (Iglesias et. al., 2007). La expresión de esta resistencia es estable en una amplia diversidad de ambientes (Presello et. al., 2006) depende de varios genes, siendo un carácter con distribución del tipo cuantitativa (Chunguet. al., 1996) y presenta una herencia compleja. Una posible forma de facilitar el desarrollo de híbridos resistentes, es la redefinición de la resistencia a la enfermedad en los componentes que la constituyen. Nuestro grupo de trabajo, obtuvo una población de mapeo conformada por 298 RILs F5 derivadas de la generación F2 de una cruza entre una línea resistente (L4637) y otra susceptible (L4674) a Fusarium spp, con la que fueron mapeados QTLs de resistencia a Fusarium verticillioides. Estudios previos que involucran a estas líneas parentales, sugieren que el espesor de pericarpio y un alto contenido de ácidos fenólicos son componentes de resistencia al ataque de F. verticillioides en grano (Fauguel, avance de Tesis: Sampietroet al, 2010).La complejidad en la cuantificación de estos caracteres dificulta la fenotipificación de ellos en toda la población de mapeo. Existen diferentes técnicas de fenotipado selectivo (selectivephenotyping) para realizar la selección de un subgrupo de líneas que minimice la pérdida de información y sensibilidad del mapeo (Jinet al, 2004; Jannink, 2005).Este trabajo se realizó con el objetivo de elegir un subgrupo de líneas que nos permita seguir detectando los QTLs de resistencia previamente identificados, para luego mapear los componentes de resistencia mencionados. MATERIALES Y METODOS Desarrollo de la Población. Las líneas L4674, parental susceptible de la población de mapeo, fue derivada del compuesto R4993 y L4637, parental resistente, fue derivada del híbrido LP561×LP611, ambas provenientes de germoplasma flint argentino y evaluadas con anterioridad en múltiples años y localidades (Presello et al, 2006). A partir de la línea F2 derivada de los parentales mencionados se generaron 298 RILs hasta la generación F4:F5. Las líneas F4 fueron utilizadas para la genotipificación y las líneas F5 para obtener los datos fenotípicos. Evaluación a campo. La población de mapeo y ambos parentales fueron evaluados en las campañas 2009/10 y 2010/11 en la Estación Experimental INTA Pergamino. Se utilizó un diseño de bloques completos aleatorizados de dos repeticiones, con parcelas de dos surcos de 5 metros cada uno, separados 90cm entre sí y a una densidad de 5 plantas por metro. Se inocularon15 plantas por parcela mediante la inyección de 2 ml de suspensión conidial a una concentración de 1×106 esporas por ml de F. verticillioidesP364, aislamiento agresivo y toxicogénico obtenido de maíz en Pergamino(Iglesias et al, 2007). Las líneas seleccionadas y ambos parentales se evaluaron por severidad de síntomas visibles de acuerdo a la escala propuesta por Reidand Hamilton (1996), donde: 1 = sin síntomas; 2 = 1- 3%; 3 = 4-10%; 4 = 11-25%; 5 = 26-50%; 6 = 51-75%; y, 7 = 76-100% del área de la espiga visiblemente afectada por podredumbre de espiga. Fenotipado Selectivo.Se definió arbitrariamente un tamaño muestral de 120 líneas para realizar el fenotipado selectivo. Se aplicaron tres procedimientos: 1) Siguiendo las pautas de Jinet. al. (2004): el criterio se basa en la comparación de los datos de marcadores moleculares para cada línea,contrastados con los datos de toda la población de mapeo, y selecciona aquel grupo de líneas que presentan la mayor disimilitud genotípica entre ellas. 2) maxRec: el procedimiento consiste en analizar pares consecutivos de marcadores moleculares. Selecciona el grupo de líneas que presentan la mayor cantidad de recombinaciones entre estos pares de marcadores (Jannink, 2005). 3) uniRec: sigue el mismo criterio de Maxrec, pero además considera la uniformidad de las recombinaciones en todo el genoma, es decir, selecciona el grupo de líneas que presentan la mayor cantidad de recombinaciones distribuidas en todo el genoma (Jannink, 2005). Para cada procedimiento desarrollamos un software con la colaboración del Lic. en Informática Ariel Giomi (CPCIBA MP:367),que nos facilitó el análisis matricial de la composición genética de los individuos. Análisis estadístico.El análisis de los datos fenotípicos para la población de mapeo y para los subgrupos de 120 líneas, se basó en un modelo lineal mixto considerando a los efectos de ambiente como fijos y a los efectos de genotipo y de repetición (bloque) dentro de ambiente como aleatorios. Para este análisis univariado se utilizó el procedimiento MIXED del programa estadístico SAS(SAS Institute, 1999). Los componentes de variancia se estimaron mediante el método de Máxima Verosimilitud Restringida (Patterson, 1997). Datos genotípicos y construcción del mapa genético. El juego de datos genotípicos para toda la población de mapeo consta de 256 marcadores SNP´s polimórficos. Para la población de mapeo y cada subgrupo de líneas, fueron estimados el orden de los marcadores y las frecuencias de recombinación con el software MapDisto 1.7.5 (Lorieuxet al, 2007) y se realizó el test χ2 para analizar las posibles segregaciones distorsionadas de los marcadores. Las frecuencias de recombinación fueron transformadas a centimorgan (cM) con la función Kosambi. Detección y estimación de QTLs combinados. Las medias fenotípicas (BLUPs) calculadas fueron usadas para el mapeo de QTLs utilizando un modelo mixturado (JiangandZeng, 1995) basándonos en que los modelos mixturados tienen mejor precisión que los mixtos cuando se quieren localizar QTLs en mapas no saturados. En el mapeo multicarácterpor intervalo compuesto (MT-CIM)se utilizó el análisis de regresión “stepwise” Modelo 6 del WinQTLCartographer V2.5 (Wang et al., 2011). Se estableció un umbral de 0.05 para seleccionar los QTLs putativos que fueron usados como cofactores y un tamaño de ventana de 10cM. El umbral para declarar significativo un QTL combinado fue LOD=2,5, con intervalos de escaneo de 2cM entre marcadores y un QTL putativo. Las posiciones de los QTLs fueron asignadas en las regiones relevantes al punto máximo del LOD. RESULTADOS Y DISCUSIONES Fenotipado Selectivo y mapas genéticos. El mapa genético de la población de mapeo ubicó 256 marcadores SNP polimórficos en 10 grupos de ligamiento que cubrieron 1178cM del genoma total.Los tres procedimientos fueron aplicados en forma separada y se obtuvieron tres subgrupos de 120 líneas cada uno, con muchas líneas en común entre ellos. En la tabla 1 se muestra el resultado de la construcción del mapa genético para la población de mapeo y para cada subgrupo de líneas obtenido con los tres procedimientos. Población de Mapeo Procedimiento Jin et al, 2004 Procedimiento maxRec Procedimiento uniRec 10 10 10 10 1178 cM 1025 cM 987 cM 1158 cM 256 198 208 231 g.l. distancia total SNP polimórficos Tabla 1. Resultados de la construcción de los mapas genéticos de los subgrupos de líneas seleccionados con los distintos procedimientos y el de la población de mapeo. En base a los resultados de la Tabla 1, decidimos realizar el análisis de QTLs para severidad de síntoma con el subgrupo de líneas seleccionado por el procedimiento uniRec, ya que la pérdida de información en relación a datos moleculares fue relativamente baja considerando que sólo utilizamos aproximadamente 2/5 de la población inicial. Detección de QTLs. En la población de mapeo se detectaron 6 QTLs en los cromosomas 1, 2, 3 y 5 (Figura 1, a). En el subgrupo de líneas seleccionado, se detectaron 6 QTLs en los cromosomas 1, 2, 3, 5 y 10 (Figura 1, b). 2 (a) 3a 3b 1 (b) 1 5a 5b 2 3b 5a 5b 10 Figura 1. Salidas del programa winQTLcart v2.5, en el análisis de QTLs asociados a severidad de síntoma para la población de mapeo (a) y el subgrupo de líneas seleccionado por el método uniRec(b). Los círculos de color claro indican aquellos QTLs que coincidieron en ambos grupos de líneas, aquellos de color oscuro son: en (a) un QTL no identificado en el subgrupo de líneas y en (b) un QTL espúreo. En ambos grupos de líneas se identificaron los QTL 1, 2, 3b, 5a y 5b para resistencia a la enfermedad ubicados en los cromosomas 1, 2, 3 y 5, mientras que para el subgrupo de 120 líneas apareció 1 QTLadicional en el cromosoma 10, el cualconsideramosespúreo.En el subgrupo de líneas no se pudo identificar el QTL 3a. Estos resultados indican que, si bien existió una pérdida en la precisión, los QTLs más importantes fueron identificados en ambas poblaciones. CONCLUSIONES La técnica de fenotipado selectivo propuesta por Jannink, denominada uniRec, fue de utilidad para seleccionar una fracción (2/5) de líneas de la población de mapeo inicial con la cual detectar QTLs de resistencia a Fusarium verticillioides.Lógicamente, trabajar con una mayor fracción de líneas, hubiese mejorado la calidad y cantidad de información, pero la elección del número de líneas (120) fue considerado teniendo en cuenta las posibilidades económicas y el tiempo disponibles. Consideramosadecuado este subgrupo de 120 líneas para continuar con el fenotipado de los componentes de resistencia, espesor de pericarpio y concentración de ácido t-ferúlico. Fuentes de financiamiento * INTA, Proyecto 52-021321 Desarrollo de germoplasma de maíz resistente a estrés biótico y abiótico (Inicio 2009, finalización y reformulación 2011) comprendido en el Proyecto Integrado PNCER 1 (inicio 2006 finalización 2014) * Beca CONICET tipo II, convocatoria 2012 CITAS BIBLIOGRAFICAS √- Chungu C., Mather D. E. , Reid L. M. and Hamilton R. I. 1996. Inheritance of kernel resistance to Fusariumgraminearum in maize. J. Hered. 87:382-385 √- Iglesias J., Presello D., Botta G., Lori G., 2007. Resistance of Argentinian Landraces to Field Accumulation of Fumonisin, Deoxynivalenol and Zearalenone.Advances in research on toxigenic fungi and mycotoxins in South America ensuring food and feed safety in a myco-globe context. Villa Carlos Paz, Córdoba, Argentina √- Jannink J.L. 2005. Selective Phenotyping to Accurately Map Quantitative Trait Loci.Crop Sci. 45:901–908 √- Jiang, C., Zeng, Z.B., 1995. Multiple trait analysis of genetic mapping for QTL. Genetics 140: 1111–1127. √- Jin C.,Lan H.,Attie A.D.,ChurchillG.A.,Bulutuglo D. yYandell B.S. 2004.Selective Phenotyping for Increased Efficiency in Genetic Mapping Studies.Genetics 168: 2285–2293. √- Lorieux, M., 2007. Map Disto, a free user-friendly program for computing genetic maps. In: Computer Demonstration (P958) Given at the Plant and Animal Genome XV Conference, San Diego, CA. √-Patterson H.D., 1997, Analysis of series of varietytrials.En R.A. Kempton, y P.N. Fox (eds.) Statisticalmethodsforplantvarietyevaluation. Chapman & Hall. √- Presello D. A., Iglesias J., Botta G., Reid L. M., Lori G. A., and Eyherabide G.H. 2006. Stability of maize resistance to the ear rots caused by Fusariumgraminearum and F. verticillioides in Argentinian and Canadian environments.Euphytica 147:403-407 √- Reid, L. M. and R. I. Hamilton. 1996. Effects of inoculation position, timing, macroconidial concentration, and irrigation on resistance of maize to F. graminearum infection through kernels. Can. J. PlantPathol. 18:279-285 √- Sampietro D. A., Vattuone M., Fauguel C., Presello D. A. y Catalán C. 2010. Evaluación de la contribución de metabolitos secundarios pericarpelares a la resistencia del maíz contra Fusarium verticillioides. XVIII Congreso Argentino de Química √- SAS Institute, 1999. The SAS Online Doc v. 8.SAS Institute, Cary, NC. √- Wang, S., Basten, C.J., Zeng, Z.B., 2011. Windows QTL Cartographer 2.5.Departmentof Statistics, North Carolina State University, Raleigh, NC.